PEMS_Soft
Bioinformatics Laboratory
BLSOMを用いたメタゲノム配列に対する系統推定
解析ソフトウェア:PEMS (Phylogenetic Estimation of Metagenomic sequence using BLSOM)†
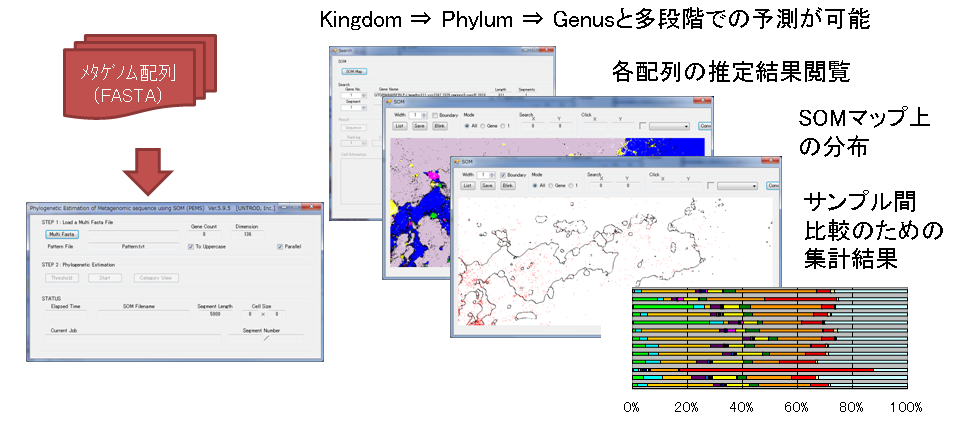
「BLSOMを用いたメタゲノム配列に対する生物系統推定解析」をワークフロー化した解析ソフトウェアPEMSを公開しました。ソフトウェアは、マルチFASTA形式の塩基配列ファイルを入力するだけで、300塩基以上の配列データに対し、Kingdom, Phylum/Class, Genusごとに作成したBLSOMマップにマッピングを行ない、3段階(Kingdom->Phylum/Class->Genus)での絞り込みによる生物系統推定を実施する(図1)。
本手法は、塩基配列の連続塩基出現頻度のみで生物系統推定可能であり、rDNAに代表されるようなオーソログ配列セットや配列アラインメントを必要としないため、新規の高いメタゲノム配列に対する生物系統推定が可能である。
出力結果としては、各配列の生物系統推定結果閲覧、各BLSOMマップ上でのマッピング結果の閲覧&画像データの保存、生物系統推定結果の集計結果を得ることができる。
ダウンロード†
- ダウンロードサイトより取得下さい。
- PCの推奨仕様
- CPU: Pentium4 2GHz 以上、デュアルコア以上もしくはハイパースレッド
- Memory: 2GB 以上
- HDD: 4GB 以上の残容量(スワップ領域は除く)
- Video: 解像度1280 x 1024 ピクセル以上、色 16ビット以上
- OS
- Microsoft Windows 7(64 bit版を推奨)
- Microsoft .NET Framework 4.0 以上のランタイム
- 【注意】
本ソフトウェアは、負荷の高い計算をスレッドで処理することによって、ユーザインターフェースのレスポンスの低下を防いでいる。シングルコアの CPU の場合、本ソフトウェアの画面の再描画やボタンなどの反応が著しく低下する。このため、CPU に関してはデュアルコア以上、もしくは、ハイパースレッド仕様の CPU の利用を推奨する。
- 【参照用BLSOMマップ情報】
- Kingdom
真核生物111種、原核生物2,813種、葉緑体110種、ミトコンドリア110種、ウイルス31,486種を対象に、断片化サイズ5kb, 縮退4連続塩基で作成したBLSOMマップを使用 - Phylum/Class
原核生物3,157種を対象に、断片化サイズ5kb, 縮退4連続塩基で作成したBLSOMマップを使用
原核生物種の配列情報は、DDBJ/EMBL/GenBankに登録されている塩基配列長が10kb以上の生物種を収集
現在は、35 Phylum/Classを対象 - Genus
上記、原核生物3,157種を各Phylum/Class別に、断片化サイズ5kb, 縮退4連続塩基で作成したBLSOMマップを使用
現在は、27 Phylum/Classに対し、Genusの推定を実施

この 作品 は クリエイティブ・コモンズ 表示 - 非営利 - 改変禁止 3.0 非移植 ライセンスの下に提供されています。
マニュアル†
- 日本語
- 特に利用する出力ファイルについて
- 「Myresult_Top.txt」:各配列ごとに、Kingdom/Phylum/Genusでの系統推定結果を出力。
- 「Myresult_Hist.txt」:「Myresult_Top.txt」の結果より、Kingdom/Phylum/Genusごとで分類名ごとに推定された件数の集計結果を出力。Kingdom/Phylum/Genusで推定できなかった件数を、「UNCLASSIFIED」として出力している。
更新履歴†
- 2012/06/19 ver. 6.6.4 公開
開発者†
- 阿部貴志 (1)、和田健之介 (2)、金谷重彦 (3)、池村淑道 (2)
(1) 新潟大学大学院自然科学研究科/工学部情報工学科
(2) 長浜バイオ大学
(3) 奈良先端科学技術大学院大学
参考文献†
- Takashi Abe, Shigehiko Kanaya, Makoto Kinouchi, Yuta Ichiba, Tokio Kozuki, and Toshimichi Ikemura. Informatics for unveiling hidden genome signatures, Genome Research, 13, 693-702, 2003.
- Takashi Abe, Hideaki Sugawara, Makoto Kinouchi, Shigehiko Kanaya, and Toshimichi Ikemura. Novel Phylogenetic Studies of Genomic Sequence Fragments Derived from Uncultured Microbe Mixtures in Environmental and Clinical Samples, DNA research, 12, 281-290. 2005.
- Hiroshi Uehara, Yuki Iwasaki, Chieko Wada, Toshimichi Ikemura and Takashi Abe. A novel bioinformatics strategy for searching industrially useful genome resources from metagenomic sequence libraries. Genes & Genetic Systems, 86, 53-66, 2011.
Counter: 8803,
today: 1,
yesterday: 1